読んだ。
Proceedings of the IEEE Computer Society: International Conference on Computer Vision and Pattern Recognition. 2005. pp. 42–47.
Food Quality and Preference, 2007, 18, 627–640.
複数の距離行列が与えられたとき、元のデータの関係をMDS やPCA っぽく2次元もしくは3次元にプロットし直す方法。
2つめの論文では、被験者10人に8種の銘柄のビールを飲んでもらって、適当にビールの種類についてグループ分けしてもらい、10人のグループ分けのパターンから元の8種のビールの「ビール空間」的なものを構築する話。
R ではDistatisR にある。
元の論文では、男女3人ずつの 人の顔から、いろいろパラメータを取ってそのパラメータに着目した時の、6人の顔の距離行列のデータがある。study とはパラメータのとり方の数で、これは
である。4つのstudy を1つのcompromise にまとめることが目標である。
表記は論文に従っている。study に関する距離行列
があって、R 上では
のアレイになっている。
DistAlgo データセットは、Pixels, Measures, Ratings, Pairwise という方法でデータをとって距離行列を作っている。
cross-product matrix を作る。いま、 で補正するベクトル
と単位行列
を用いて
となるを作る。これは
ごとにある。
は
の正方行列なので、特異値分解して固有値の1つめで割って補正した
を用意する。
library(DistatisR) data(DistAlgo) St <- function(arr){ Imat <- diag(1, nrow(arr)) M <- Imat - matrix(1, nr=nrow(arr)) %*% t(m) res <- mapply(function(z){ S <- -1/2 * M %*% DistAlgo[,,z] %*% t(M) eiS <- eigen(S) Snorm <- S/eiS$values[1] }, 1:dim(arr)[3], SIMPLIFY=FALSE) return(res) } Snorm <- St(DistAlgo) names(Snorm) <- dimnames(DistAlgo)[[3]]
いま、 は
のアレイ(R ではリストにしている)だが、いわゆるR で普通にやるようなベクトル化して、列ベクトル
がstudy 分あるベクトル
を作る。
次元である。
X <- sapply(Snorm, c) # complete data matrix
compromise matrix を作るが、これは各study での距離行列同士の相関 とみなせる。
はcongruence, monotonicity とか言われる。
ベクトル化した を利用して、
となる行列
を作る。正規化して-1~1 に収まる感じにしようと思ったら、内積とcos を使って
ただし
という相関行列を作る。これは
と同じことである。
A <- t(X) %*% X # studies scalar product matrix N <- diag(diag(A)) n <- apply(X, 2, norm, "2") C <- A/outer(n, n, "*") Rv <- A/sqrt(outer(diag(A), diag(A), "*"))
行列 は正方な相関行列であり、PCA でいうところの共分散行列みたいなものだから、特異値分解してPCA っぽく主成分をプロットできる。
適当に回転してしまったことに注意。
また、PCA と同じことをしているので、分散により各主成分がどれくらい説明能力があるかを定量できる。
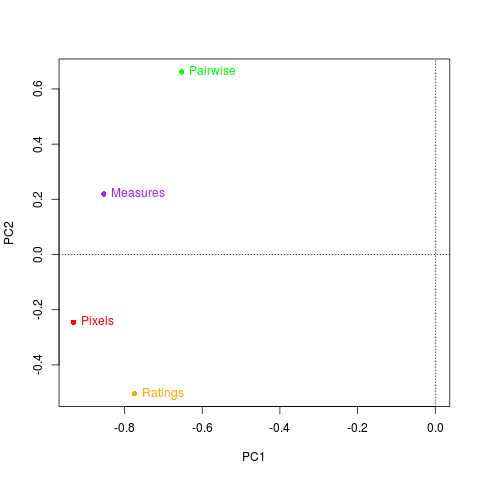
eiC <- eigen(C) G <- eiC$vectors %*% diag(eiC$values^(1/2)) rownames(G) <- dimnames(DistAlgo)[[3]] cols <- c("red", "purple", "orange", "green") plot(G[,1:2], pch=16, xlim=range(G[,1], 0), xlab="PC1", ylab="PC2", col=cols) text(G[,1:2], rownames(G), pos=4, col=cols) abline(v=0, h=0, lty=3)
eiC$values/sum(eiC$values)
[1] 0.65528859 0.20015228 0.12116261 0.02339652
各study がどんなものかの説明がついたので、study を統合してひとつの結果(compromize) を出しにかかろう。いま、 を特異値分解して得られた固有ベクトルの行列
のうち、第一固有ベクトルに着目する。これにより、重み係数
を求める。これはすべてのstudy
について求められるから
を求める。 は
行列である。
これもまた、特異値分解されて となる
と
があって、compromise factor なる
は
になる。
を特異値分解した主成分をプロットすれば、それぞれのstudy の距離行列をまとめたときの、元のサンプルたちの関係がわかる、ということになる。
論文では、PC1 は男女をわけており、PC2 はちょっとよくわからないが、髪が明るい人と、髪が濃いもしくはハゲの人をわけている。
P <- eiC$vectors alpha <- sweep(P, 2, colSums(P), "/") Splus <- matrix(rowSums(sweep(X, 2, alpha[,1], "*")), nrow(DistAlgo)) eiSplus <- eigen(Splus) Fscore <- eiSplus$vectors %*% diag(eiSplus$values^(1/2)) plot(eiSplus$vectors[,1:2], type="n", xlab="PC1", ylab="PC2") text(eiSplus$vectors[,1:2], dimnames(DistAlgo)[[1]]) abline(v=0, h=0, lty=3) legend("topright", legend=names(Snorm), lty=1, col=cols)

もとのstudy ごとの距離行列がどれくらい寄与していたのかを考える。,
,
であることを利用すると、
となる。
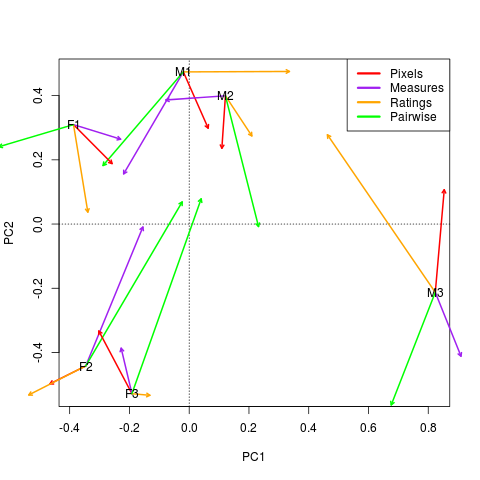
はstudy
ごとの寄与率みたいなものである。プロットするとFigure 5 ができる。
ここで、 は
列までしかない。というのも、
を特異値分解した時点で、6番目の固有値は0となっている。特異値分解を繰り返しまくっているから一次独立でなくなるのか、主成分を全部集めれば説明できる度合いが1 になるのでここで1つパラメータが落ちるのか、たぶんそんなやつ。
また、特異値分解すると微妙に論文と値が違うのだが、R では不偏分散で計算しているので、もしかしたら論文では分散で計算しているのかもしれない(未確認で進行形
F1 とM3 の男女を見ると、Pixels, Measures, Ratings, Pairwise の4つのstudy が見事にすべて逆を向いているのがわかるし、F2 とF3 のよく似た女性は、Measures とPairwise が近いということがわかる。
Fs <- lapply(Snorm, "%*%", eiSplus$vectors %*% diag(eiSplus$values^(-1/2))) plot(eiSplus$vectors[,1:2], type="n", xlab="PC1", ylab="PC2") abline(v=0, h=0, lty=3) legend("topright", legend=names(Snorm), lty=1, col=cols, lwd=3) for(i in 1:nrow(eiSplus$vectors)){ for(j in seq(Fs)){ x0 <- eiSplus$vectors[i, 1] y0 <- eiSplus$vectors[i, 2] x1 <- Fs[[j]][i, 1] y1 <- Fs[[j]][i, 2] arrows(x0, y0, x1, y1, xpd=TRUE, col=cols[j], length=0.05, lwd=2) } } text(eiSplus$vectors[,1:2], dimnames(DistAlgo)[[1]])